La révolution CRISPR ?
Dans un News Focus de Science Pennisi, E. (2013) intranet.pdf fait un petit historique de la découverte d'un mécanisme de protection des bactéries contre les virus. Il en résulte une technique et un pan nouveau de recherche qui se développe exceptionnellement rapidement et mérite l'attention des abonnés aux Bio-Tremplins. C'est en cherchant à protéger les bactéries qui font le yoghourt (Streptococcus thermophilus p. ex.) dans l'industrie laitière danoise que des chercheurs ont réussi à booster les défenses bactériennes en présentant aux bactéries l'ADN des virus. Forts des techniques de séquençage et de bioinformatique actuelle, ils ont contribué à élucider ce mécanisme, parfois comparé à un système immunitaire bactérien (cf fig1). CRISPR est constitué d'un ARN guide constant, attaché à une séquence spécifique de l'ADN à cibler, et d'une protéine Cas9 qui accueille cet ARN et guide le positionnement de cet ARN sur l'ADN-cible et découpe les deux brins d'ADN à la position correspondante. Cf par exemple Brouns, S. J. J., et al. (2008). intranet.pdf Comment Obtenir un article mentionné : Get-a-doi
Fig 1: Quand des virus (en vert) attaquent une bactérie, elle déploie des défenses contre l'ADN viral que les biologistes ont appris a utiliser pour le génie génétique [img] source Pennisi, E. (2013): EYE OF SCIENCE/SCIENCE
En quelques mois des chercheurs du monde entier ont pu exploiter sa spécificité et sa simplicité pour intervenir dans les génomes directement ou en modifiant la protéine.
UniProt - la célèbre base de protéines basée à Genève a publié 2 headlines sur le sujet :
- Latest from the prokaryotic world: bacterial Cas9, a new tool for genome engineering
- Prokaryotes do it too: CRISPR, an RNA-based adaptive immune system
CRISPR : Un ARN en deux parties et une protéine
CRISPR est constitué d'un ARN guide, en partie palindrome (définition ici) constant, attaché à une séquence ARNcr spécifique de l'ADN à cibler, et d'une protéine Cas9 (cf. fig 2) qui accueille cet ARN et guide le positionnement sur l'ADN-Cible et découpe les deux brins à la position correspondant à la fin de la séquence guide.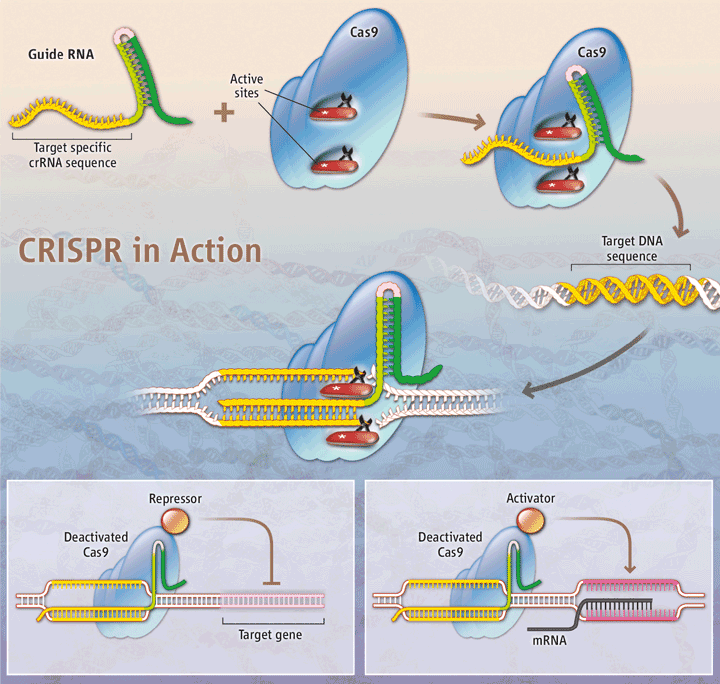
Fig 2 : Le mécanisme d'action de CRISPR est simple et modulaire . Cliquer pour agrandir. Il est développé plus bas [img] source : Pennisi (2013)
Chez les bactéries ce sytème permet en intégrant de courts fragments d'ADN étranger dans le système CRISPR d'armer la bactérie contre de nouvelles attaques de ce même agent pathogène (Virus, mais aussi plasmides, éléments conjuguants, ou transposables) . C'est ce qui a sauvé les cultures de bactéries dans l'industrie laitière Danoise…
"Resistance is acquired by incorporating short stretches of invading DNA sequences in genomic CRISPR loci " Brouns, S. J. J., et al. (2008)
Un système simple et polyvalent
La simplicité de ce système permet de fabriquer des ARN ciblant à volonté des séquences très spécifiques chez divers organismes, de les accoler au palindrome, et pour autant que Cas9 soit présent l'ADN sera coupé à l'endroit spécifique. Ce système n'est pas sans rappeler l'ARN interférant des Eukaryotes (cf Bio-Tremplins un commando de 9 prend le contrôle de 273 )La polyvalence du système est exprimée dans l'illustration de Science (fig. 2) qui figure chacun des sites actifs de Cas9 comme un couteau suisse

- Cas9 chez UniProt G3ECR1 CRISPR-associated endonuclease Cas9 Streptococcus thermophilus (1,409 bases)
Par exemple en associant un répresseur à Cas9, ils ont pu bloquer un gène spécifié par la séquence d'ARN associée à Cas9 (cf. Fig 3.gauche) . En associant un promoteur, ils ont pu activer un gène spécifique (cf. Fig 3.droite) .

Fig 3 : Les chercheurs on pu exploiter le mécanisme d'action de CRISPR en modifiant la protéine Cas9 pour spécifiquement activer ou réprimer l'expression d'un gène. [img] source : K. SUTLIFF/SCIENCE in Pennisi (2013)
Modulaire et spécifique, ce système permet de nombreuses applications en génie génétique
En modifiant la protéine Cas9 d'autres chercheurs ont pu effectuer à l'endroit spécifié par l'ARN guide d'autres interventions comme bloquer un gène – en associant un répresseur à Cas9, activer un gène – en associant un promoteur, ou ouvrir l'ADN ( "nick") en supprimant un des sites actifs – pour insérer un ADN thérapeutique à un endroit précis.
Fig 4: En 8 mois on a pu montrer l'efficacité du système CRISPR chez divers organismes (Caenorhabditis elegans, Danio rero, Drosophila) [img] source Pennisi (2013) CREDITS (TOP TO BOTTOM): FRIEDLAND ET AL., NATURE METHODS 10 (JUNE 2013); ANDREW GONZALES/JOANNA YEH; SCOTT GRATZ/UNIVERSITY OF WISCONSIN, MADISON
Fig 4: En 8 mois on a pu montrer l'efficacité du système CRISPR chez divers organismes (Caenorhabditis elegans, Danio rero, Drosophila) [img] source Pennisi (2013) CREDITS (TOP TO BOTTOM): FRIEDLAND ET AL., NATURE METHODS 10 (JUNE 2013); ANDREW GONZALES/JOANNA YEH; SCOTT GRATZ/UNIVERSITY OF WISCONSIN, MADISON
Ouais ... ces séquences on peut les voir m'sieur ?
Qu'un élève ait encore assez de curiosité pour poser cette question est rare, mais le principe d'accès libre à l'information imposé par les revues scientifiques entre autres implique qu'on peut accéder aux séquences de toute recherche publiée (Cf BIST) et adopter une démarche expérimentale et satisfaire le scepticisme de cet élève : vérifier sur la base de données cette affirmation...Marie-Claude Blatter du SIB nous rappelle que " Le cr RNA est composé d'une séquence 'spacer' spécifique et d'une séquence palindrome." Par exemple dans Brouns, S. J. J. et al (2008) on trouve :

D'autre part, elle nous indique Palindrome search un outil qui permet de détecter les séquences palindromiques: http://bioinfo.cs.technion.ac.il/projects/Engel-Freund/new.html (! il faut mettre la séquence en format fasta c'est à dire précéder la séquence par une ligne qui commence avec un > suivi d'une description - en fait on peut mettre n'importe quoi après le >)
Si on insère dans l'outil à détecter les palindromes la séquence trouvée ci-dessus - dûment labellisée pour FASTA :
>E coli CRISPR
gagttccccgcgccagcggggataaaccgctttcgcagacgcgcggcgatacgctcacgca
on découvre bien un palindrome :
5 TCCCCGCG 12
|||||||
22 AGGGGCGA 15Autre exemple plus récent
Dans un papier récent Chen, et al. (2013)Comment Obtenir un article mentionné : Get-a-doi ont modifié C. elegans , et on trouve dans les supplementary data ici la séquence guide qui permet la fixation de l'ARN sur la protéine Cas9 dûment labellisée en format fasta :>Exemple pris chez Chen pour modifier C. elegans
GTTTTAGAGCTAGAAATAGCAAGTTAAAATAAGGCTAGTCCGTTATCAACTTGAAAAAGTGGCACCGAGTCGGTGCT
Si on insère dans Palindrome search cette séquence on trouve
61 GGCACCGA 68
|||||||
77 TCGTGGCT 70
D'autres exemples
M.-C. Blatter nous indique comment trouver quelques cr RNA spacer dans GenBank: (la sequence spacer qui reconnaît la cible) : http://www.ncbi.nlm.nih.gov/nuccore/?term=%22crispr+rna%22
Trop compliqué pour les élèves ?
Peut-être… il est surtout nouveau pour les enseignants et n'est pas encore entré dans les pratiques enseignantes ( transposition didactique à faire ?) D'une autre coté le système CRISPR n'est pas bien complexe et par sa nouveauté il peut renouveler les exemples, les exercices voire les évaluations…
Des articles vulgarisés en français ?
Sources :
- Chen, Changchun, Lorenz A. Fenk, Mario de Bono. (2013) Efficient genome editing in Caenorhabditis elegans by CRISPR-targeted homologous recombination Nucl. Acids Res. first published online September 5, 2013 doi:10.1093/nar/gkt805
- Brouns, S. J. J., Jore, M. M., Lundgren, M., Westra, E. R., Slijkhuis, R. J. H., Snijders, A. P. L., … van der Oost, J. (2008). Small CRISPR RNAs Guide Antiviral Defense in Prokaryotes. Science, 321(5891), 960‑964. doi:10.1126/science.1159689 | intranet.pdf
- Pennisi, E. (2013). The CRISPR Craze. Science, 341(6148), 833‑836. doi:10.1126/science.341.6148.833 | intranet.pdf
Mise à jour 5 Nov 21 correction de liens devenus obsolete


Bonjour,
RépondreSupprimerPensez vous que cette technologie CRISPR puisse enfin résoudre le problème des maladies génétiques et si oui en combien d'années environ.
Merci.
On ne peut que dire que ça va sans doute aider dans les recherches. On ne peut rien prédire en biologie fondamentale.
SupprimerMerci pour cet article, qui contient des vraies références, et une explication claire mais détaillée de ce système! Ayant besoin de renseignements là dessus pour l'écriture d'un prochain article, votre post est parfait!
RépondreSupprimerJ'ai un fils qui a la leucinose une maladie génétique du métabolisme qui demande une diète hypoprotéiné toute sa vie. Cela est causée par un gène défectueux chez moi et ma conjointe et j'espère de tout coeur que cette découverte pourra nous aider un jour pour corriger le gène défectueux et plusieurs autres maladies du métabolisme . Très belle découverte.
RépondreSupprimer